- Splicing alternativo
-
El splicing alternativo (alternative splicing en inglés) o empalme alternativo permite obtener a partir de un transcrito primario de mRNA o pre-ARNm distintas moléculas de mRNA maduras. Este proceso ocurre principalmente en eucariotas, aunque también puede observarse en virus.
Contenido
Introducción
Al transcribirse el ADN a ARNm se obtiene un transcrito primario de ARN o pre-ARNm que incluye intrones y exones. Para que este pre-ARNm de lugar a un ARNm debe sufrir un proceso de maduración del ARNm, que consiste, básicamente, en eliminar todos los intrones. Sin embargo los intrones y exones no siempre están determinados durante el proceso de ayuste. La selección de los sitios de ayuste es llevado a cabo por residuos de serina/arginina de ciertas proteínas conocidas como proteínas SR.
Tipos de splicing alternativo
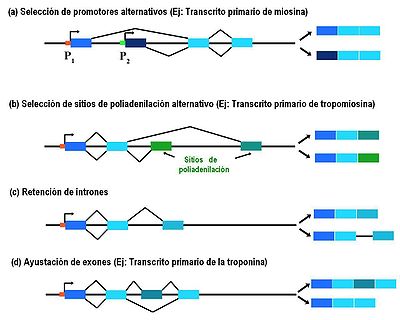
(a) Selección de promotores alternativos: este es el único método que da lugar a un dominio N-terminal alternativo. En este caso, cada promotor puede dar lugar a un juego de exones diferentes.
(b) Selección de sitios de poliadenilación alternativos: este es el único método que da lugar a un dominio C-terminal alternativo. En este caso, cada sitio de poliadenilación puede dar lugar a un juego de exones diferentes.
(c) Retención de intrones: en este caso en lugar de ayustar los intrones, estos son retenidos en el transcrito. Este intrón puede expresarse, dar lugar a un codón de parada o cambiar la pauta de lectura.
(d) Splicing de exones(exon splicing): en este caso ciertos exones son sujetos a splicing fuera.
Importancia en genética molecular
El splicing alternativo invalida la vieja teoría “un gen una proteína”, siendo por tanto necesario información externa para decidir que polipéptido será sintetizado. Al mismo tiempo este sistema permite almacenar la información de forma más económica. Así, por ejemplo, este sistema permite obtener varias proteínas a partir de una única secuencia de ADN.
Algunos investigadores han sugerido que este sistema permitiría obtener nuevas proteínas cambiando los mecanismos de regulación. También se ha sugerido que este sistema permitiría una evolución más rápida.
Existe una creencia que afirma que los sitios alternativos de splicing son responsables de la complejidad de los humanos; afirmando que los genes humanos tienen más sitios alternativos de splicing. Sin embargo un estudio de David Brett y colaboradores[1] afirma que no existen diferencias significativas entre el número de sitios de splicing alternativos de humanos con otros animales. Actualmente el récord de sitios alternativos de splicing lo tiene el gen Dscam de Drosophila con 38.000 variantes de splicing.
Véase también
Referencias
- ↑ David Brett; Heike Pospisil; Juan Valcárcel; Jens Reich; Peer Bork (17 de diciembre de 2001). «Alternative splicing and genome complexity». Nature Genetics 30: pp. 29-30. doi:. http://www.nature.com/ng/journal/v30/n1/abs/ng803.html;jsessionid=BF0AED8347574D063F5E347EC693AE83.
Enlaces externos
- HHMI article on alternative splicing
- Study on alternative splicing and complexity
- Stamms-lab.net: Research Group dealing with alternative Splicing issues and mis-splicing in human diseases
- Alternative Splicing of ion channels in the brain, connected to mental and neurological diseases
- Alternative Splicing definition at English Wikipedia
Wikimedia foundation. 2010.